L’alphabet de la vie et ses combinaisons
L’existence humaine s’écrit à l’échelle microscopique sous la forme d’un alphabet fondamental composé de quatre lettres spécifiques. Ces nucléotides se nomment l’adénine (A), la cytosine (C), la guanine (G) et la thymine (T). À l’intérieur du corps, ces éléments s’associent pour former ce que les biologistes appellent des codons, des séquences lues par groupes de trois lettres qui indiquent aux cellules quel acide aminé intégrer lors de la fabrication d’une protéine.
La lecture de ce code obéit à des règles mathématiques précises, offrant un total de 64 combinaisons possibles de codons. Parmi celles-ci, 61 sont destinées à coder des acides aminés. Les trois dernières combinaisons, identifiées sous les séquences UAA, UAG et UGA, exercent une fonction radicalement différente. Elles agissent comme des signaux d’arrêt qui marquent la fin du processus de synthèse des protéines.
Le mythe des codons synonymes interchangeables

Dans ce système de combinaisons, il arrive fréquemment que plusieurs codons différents codent pour un seul et même acide aminé. Ces éléments portent le nom de codons synonymes. Pendant une longue période, la communauté scientifique a considéré que ces séquences génétiques étaient strictement interchangeables, pensant qu’elles remplissaient exactement la même fonction sans la moindre distinction.
Cette perception théorique a récemment évolué face aux nouvelles observations en laboratoire. Les chercheurs ont constaté que l’efficacité de ces codons synonymes varie considérablement lorsqu’il s’agit d’aider l’ARN messager (ARNm) à rester stable et à se traduire correctement. L’observation montre que si un ARNm contient de nombreux codons synonymes qualifiés de non optimaux, le processus de traduction perd en efficacité.
Le mécanisme exact par lequel les cellules parvenaient à déterminer ce résultat demeurait jusqu’à présent inconnu. La manière dont le corps opère le tri entre ces différentes séquences constituait une zone d’ombre dans la compréhension de la biologie humaine.
La découverte japonaise autour de la protéine DHX29

Une étude récente publiée dans la revue Science vient de mettre en lumière l’existence d’une couche secrète dans l’ADN humain, responsable du comportement de ces différents codons synonymes. Ces travaux ont été menés conjointement par des chercheurs de l’Université de Kyoto et de l’institut RIKEN situé à Wako, au Japon.
Pour mener à bien cette exploration moléculaire, l’équipe a utilisé la technologie d’édition génétique CRISPR afin d’analyser l’expression des gènes liée aux codons. Leurs recherches se sont rapidement resserrées autour d’une protéine spécifique de liaison à l’ARN, nommée DHX29. Les expériences complémentaires ont permis d’établir que les codons non optimaux s’accumulaient en l’absence de cette protéine, indiquant son rôle central dans la régulation de ce processus inédit.
« Ces découvertes révèlent un lien moléculaire direct entre le choix des codons synonymes et le contrôle de l’expression des gènes dans les cellules humaines », a déclaré Masanori Yoshinaga, co-auteur de l’étude à l’Université de Kyoto, dans un communiqué de presse.
La cryo-microscopie électronique dévoile le mécanisme
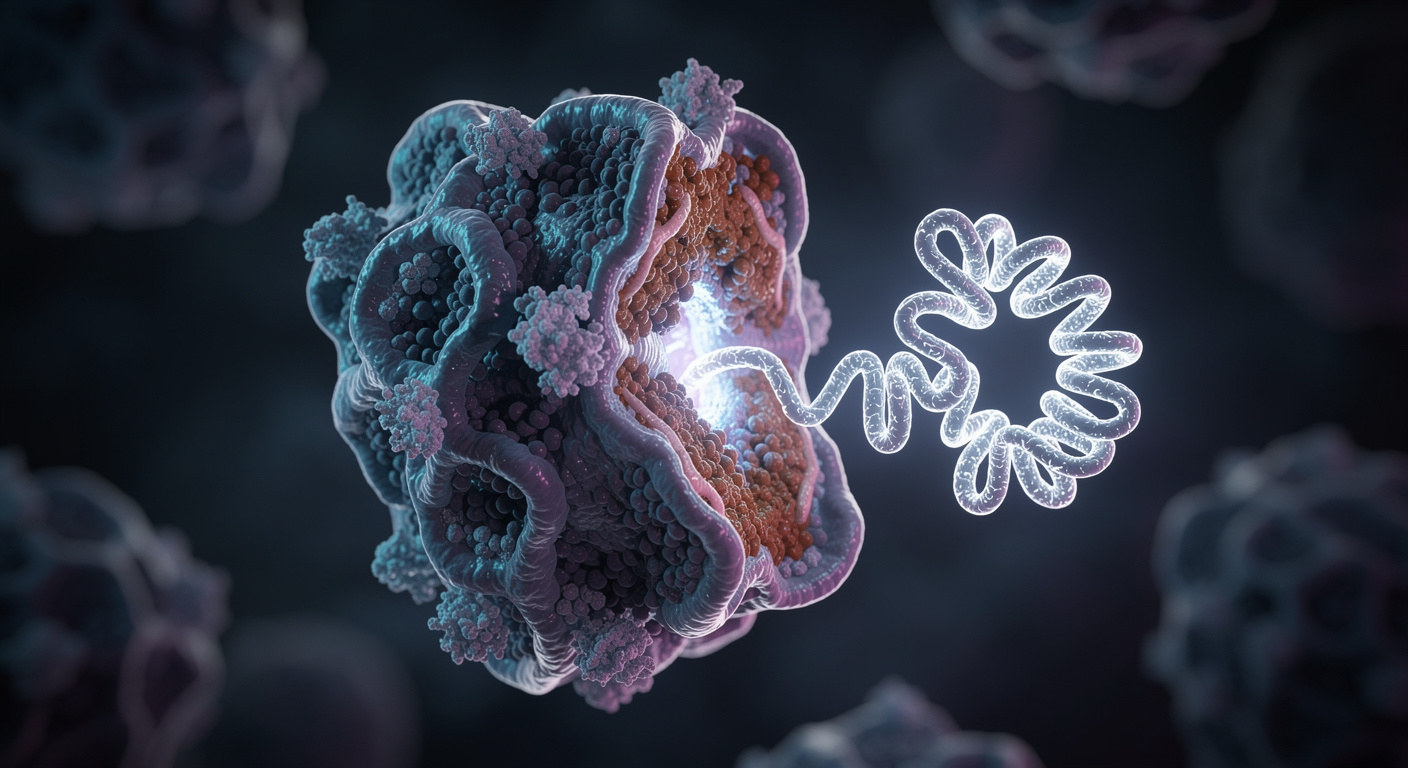
La compréhension du mode d’action de la protéine DHX29 a nécessité l’emploi d’une technologie d’observation avancée : la cryo-microscopie électronique. Également appelée cryo-ME, cette technique consiste à congeler instantanément les échantillons avant de les sonder avec des faisceaux d’électrons. Cette méthode permet de générer des images en trois dimensions de l’ADN, de l’ARN, des protéines, des virus et des cellules, se montrant particulièrement efficace pour capturer les interactions entre ces structures microscopiques.
L’observation de DHX29 a mis en évidence son interaction directe avec les ribosomes 80S, les machines cellulaires responsables de la synthèse des protéines à l’intérieur des cellules humaines. Ces données visuelles ont été croisées avec des analyses protéomiques ultérieures pour dresser un tableau complet du phénomène en cours d’étude.
Les résultats montrent que DHX29 se lie aux ribosomes qui décodent les codons non optimaux. La protéine recrute alors un complexe protéique particulier, désigné sous le nom de GIGYF2•4EHP. Le rôle de ce complexe est de supprimer l’ARNm rempli de ces codons. En identifiant les molécules d’ARNm paresseuses chargées de codons non optimaux, DHX29 les signale en vue de leur élimination pure et simple.
Différenciation cellulaire et implications pour la santé
« Nous avons longtemps été fascinés par la façon dont les cellules interprètent la couche cachée d’informations intégrée dans le code génétique », a expliqué Osamu Takeuchi, auteur principal de l’étude à l’Université de Kyoto, lors d’un communiqué de presse. Il a précisé que « découvrir le facteur moléculaire qui permet aux cellules humaines de lire et de répondre à ce code caché a donc été particulièrement gratifiant. »
Cette avancée scientifique ouvre des perspectives majeures en matière de biologie humaine, particulièrement en ce qui concerne le développement du cancer et la différenciation cellulaire, deux processus dans lesquels la protéine DHX29 joue un rôle actif. La mise en lumière de cette couche cachée de l’ADN offre aux chercheurs un nouvel outil pour analyser ces mécanismes de santé complexes.
Alors que les quatre nucléotides constituant les éléments de base de la vie pouvaient paraître simples dans leur conception initiale, les recherches biologiques démontrent continuellement que leur fonctionnement interne s’avère hautement élaboré et loin d’avoir livré tous ses secrets.
Selon la source : popularmechanics.com